首張芳香型聚酮全景圖問世
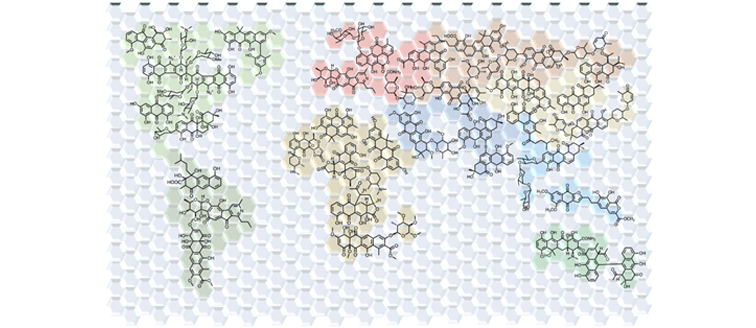
芳香型聚酮的全景圖(示意圖)西湖大學供圖
芳香型聚酮化合物的世界 西湖大學供圖
西湖大學特聘研究員張驪駻團隊探究了細菌來源的芳香型聚酮化合物的進化過程及其結構多樣性,繪制出世界上首張芳香型聚酮的全景圖。近日,該項成果發表于《德國應用化學》,論文的通訊作者為張驪駻,共同第一作者為西湖大學博士生陳閃沖和助理研究員張馳。
張驪駻這次挑戰的是聚酮化合物家族里的一類——細菌來源的芳香型聚酮化合物——它是許多重要藥物的核心成分,包括治療腫瘤的阿霉素和抗菌藥四環素,同時因為它的合成“生產線”很特殊、是多個酶協調負責合成產物,“預測”難度非常大。 傳統的藥物發現方法,即從動植物、微生物中,一個一個分離鑒定出新的天然產物,逐個研究學習的方法,只能積累個別案例,無法高效給出答案。但生物信息學,即利用計算機搜索、處理和利用生物學數據的研究方法,給天然產物的發現帶來了曙光。
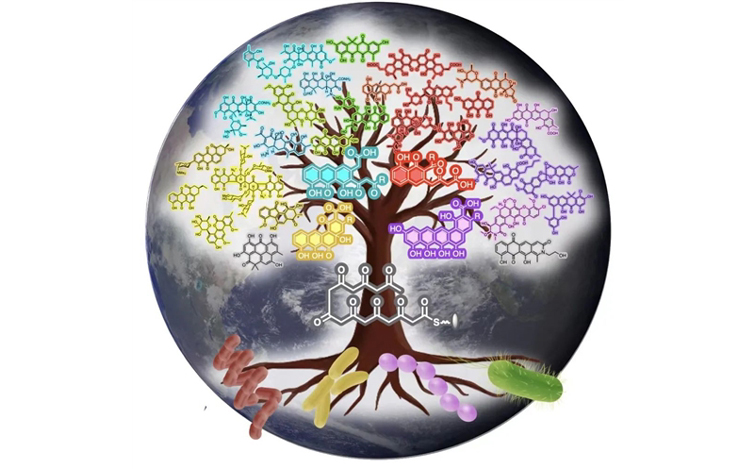
基于團隊的前期研究與資料分析,張驪駻團隊認為,芳香型聚酮分子生物合成過程中, CLF(Chain Length Factor,鏈長因子)這種酶發揮了關鍵作用。每個聚酮分子都需要這個酶,并且不同類型聚酮分子的CLF酶,會有不同的氨基酸序列。 研究團隊將目光投向167個已經被研究過(即已表征)、已知曉天然產物對應關系的基因簇(即細菌菌株中編碼生物合成酶的一列或幾類基因)。他們分析發現,這些基因簇中CLF蛋白的氨基酸序列的信息特征,正好對應著不同的化合物的結構特征。同時,同借助CLF這座“橋梁”,研究團隊得出了一個能夠“拍板”該基因簇是否能產生不同化合物的計算方法及數值線,88%——將兩個CLF的氨基酸序列作比較,88%以上都一樣的話,意味著它們最終合成產物化合物也是一樣的;低于88%,則會產生不同化合物——由此預測了最終化合物的“唯一性”。
研究團隊從公共基因組數據庫中,進一步提取了3254個細菌來源的芳香型聚酮化合物的生物合成酶的數據——這3254個酶,源自現今已被測序的全球所有的微生物(細菌)。接著,他們將第一步的研究辦法,應用到了這3254個酶上,構建出了描述“酶氨基酸序列-化合物結構”對應關系的全球“系統發育樹”。同時,他們將細菌菌株信息納入圖表,進而又得到了菌株與化合物之間的對應關系。
基于這張藍圖式的圖表,團隊分析了芳香型聚酮的全球豐度、分布和結構多樣性。由此,他們預估了自然界的總芳香型聚酮分子數量——也就是細菌來源芳香型聚酮天然產物的“人口數”,大約3000。
通過進一步分析,他們篩選出了7種菌株,鎖定了兩種能產生新型聚酮化合物的細菌。通過在實驗室中進行菌株培養,他們在這兩種菌株發酵后形成的最終產物中,均鑒定出了新型的芳香聚酮分子,包括從一株罕見嗜酸放線菌中分離得到了帶有新穎骨架的萘吡喃類化合物oryzanaphthopyran。這些發現,最終反過來佐證了本研究所取得的全景圖在這類天然產物研究中的實際價值。
相關論文信息:https://doi.org/10.1002/anie.202202286